Nat Med | Usa ka pamaagi sa multi-omics sa pagmapa sa integrated tumor, immune ug microbial landscape sa colorectal cancer nagpadayag sa interaksyon sa microbiome sa immune system
Bisan tuod ang mga biomarker para sa primary colon cancer kay gitun-an pag-ayo sa bag-ohay nga mga tuig, ang kasamtangang mga klinikal nga giya nagsalig lamang sa tumor-lymph node-metastasis staging ug detection sa DNA mismatch repair (MMR) defects o microsatellite instability (MSI) (dugang pa sa standard pathology testing) aron mahibal-an ang mga rekomendasyon sa pagtambal. Namatikdan sa mga tigdukiduki ang kakulang sa asosasyon tali sa gene expression-based immune responses, microbial profiles, ug tumor stroma sa Cancer Genome Atlas (TCGA) colorectal cancer cohort ug patient survival.
Samtang nag-uswag ang panukiduki, ang quantitative characteristics sa primary colorectal cancer, lakip na ang cancer cellular, immune, stromal, o microbial nga kinaiya sa kanser, gitaho nga adunay dakong kalambigitan sa clinical outcomes, apan limitado gihapon ang pagsabot kon giunsa makaapekto ang ilang interaksyon sa mga resulta sa pasyente.
Aron masusi ang relasyon tali sa phenotypic complexity ug outcome, usa ka grupo sa mga tigdukiduki gikan sa Sidra Institute of Medical Research sa Qatar bag-o lang nagpalambo ug nag-validate sa usa ka integrated score (mICRoScore) nga nag-ila sa usa ka grupo sa mga pasyente nga adunay maayong survival rates pinaagi sa paghiusa sa mga kinaiya sa microbiome ug immune rejection constants (ICR). Ang grupo nagpahigayon og komprehensibo nga genomic analysis sa mga presko nga frozen sample gikan sa 348 ka mga pasyente nga adunay primary colorectal cancer, lakip ang RNA sequencing sa mga tumor ug gipares nga himsog nga colorectal tissue, whole exome sequencing, deep T-cell receptor ug 16S bacterial rRNA gene sequencing, nga gidugangan sa whole tumor genome sequencing aron mas mailhan ang microbiome. Ang pagtuon gipatik sa Nature Medicine isip "An integrated tumor, immune and microbiome atlas of colon cancer".

Artikulo nga gipatik sa Nature Medicine
Kinatibuk-ang Pagtan-aw sa AC-ICAM
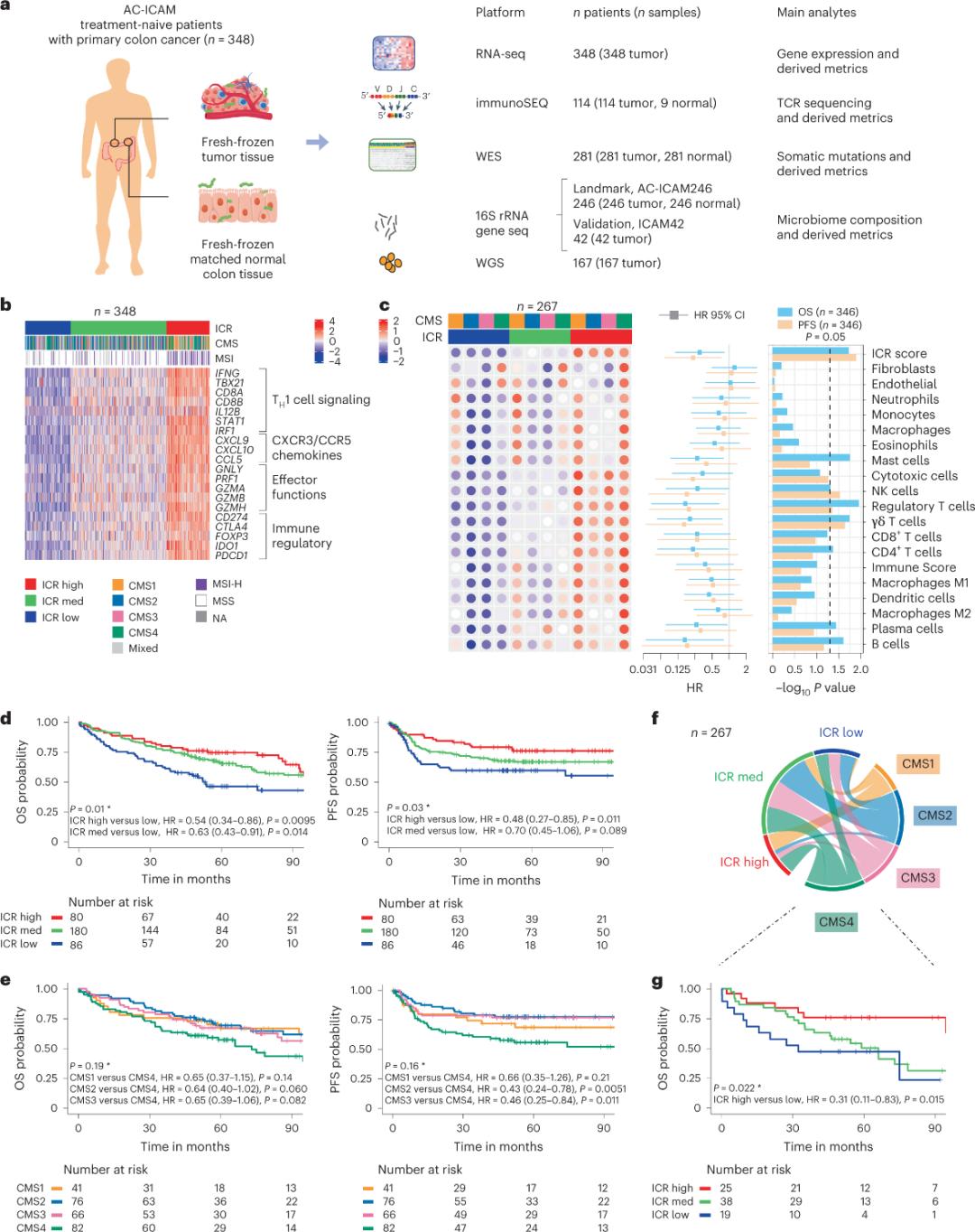
Gigamit sa mga tigdukiduki ang usa ka orthogonal genomic platform aron analisahon ang presko nga frozen nga mga sample sa tumor ug gipares ang kasikbit nga himsog nga tisyu sa colon (mga pares nga normal sa tumor) gikan sa mga pasyente nga adunay histologic diagnosis sa kanser sa colon nga wala’y systemic therapy. Base sa whole-exome sequencing (WES), RNA-seq data quality control, ug inclusion criteria screening, ang genomic data gikan sa 348 ka mga pasyente gipadayon ug gigamit alang sa downstream analysis nga adunay median follow-up nga 4.6 ka tuig. Ginganlan sa research team kini nga resource nga Sidra-LUMC AC-ICAM: A map and guide to immune-cancer-microbiome interactions (Figure 1).
Klasipikasyon sa molekula gamit ang ICR
Pinaagi sa pagkuha sa usa ka modular set sa immune genetic markers para sa padayon nga cancer immunosurveillance, nga gitawag og immune constant of rejection (ICR), gi-optimize sa research team ang ICR pinaagi sa pag-condense niini ngadto sa usa ka 20-gene panel nga naglangkob sa lain-laing mga klase sa kanser, lakip ang melanoma, kanser sa pantog, ug kanser sa suso. Ang ICR nalambigit usab sa tubag sa immunotherapy sa lain-laing mga klase sa kanser, lakip ang kanser sa suso.
Una, gi-validate sa mga tigdukiduki ang ICR signature sa AC-ICAM cohort, gamit ang ICR gene-based co-classification approach aron ma-classify ang cohort ngadto sa tulo ka cluster/immune subtypes: high ICR (hot tumors), medium ICR ug low ICR (cold tumors) (Figure 1b). Gi-characterize sa mga tigdukiduki ang immune propensity nga nalangkit sa consensus molecular subtypes (CMS), usa ka transcriptome-based nga klasipikasyon sa colon cancer. Ang mga kategorya sa CMS naglakip sa CMS1/immune, CMS2/canonical, CMS3/metabolic ug CMS4/mesenchymal. Gipakita sa pag-analisar nga ang mga ICR score negatibo nga nakig-correlate sa pipila ka cancer cell pathways sa tanang CMS subtypes, ug ang positibo nga mga correlation sa immunosuppressive ug stromal-related pathways naobserbahan lamang sa mga tumor sa CMS4.
Sa tanang CMS, ang kadaghan sa natural killer (NK) cell ug T cell subsets kay pinakataas sa ICR high immune subtypes, nga adunay mas dakong variability sa ubang leukocyte subsets (Figure 1c). Ang ICR immune subtypes adunay lain-laing OS ug PFS, nga adunay progresibong pagtaas sa ICR gikan sa ubos ngadto sa taas (Figure 1d), nga nagpamatuod sa prognostic nga papel sa ICR sa colorectal cancer.
Hulagway 1. Disenyo sa pagtuon sa AC-ICAM, pirma sa gene nga may kalabutan sa resistensya, mga subtype sa resistensya ug molekular ug pagkabuhi.
Ang ICR mokuha sa mga tumor-enriched, clonally amplified T cells
Gamay ra nga bahin sa mga T cell nga misulod sa tisyu sa tumor ang gitaho nga espesipiko alang sa mga tumor antigen (ubos sa 10%). Busa, ang kadaghanan sa mga intra-tumor T cell gitawag nga bystander T cells (bystander T cells). Ang pinakakusog nga korelasyon sa gidaghanon sa mga conventional T cells nga adunay produktibong TCRs naobserbahan sa stromal cell ug leukocyte subpopulations (nakita sa RNA-seq), nga magamit sa pagbanabana sa mga T cell subpopulations (Figure 2a). Sa mga ICR cluster (kinatibuk-an ug CMS classification), ang pinakataas nga clonality sa immune SEQ TCRs naobserbahan sa ICR-high ug CMS subtype CMS1/immune groups (Figure 2c), nga adunay pinakataas nga proporsyon sa ICR-high tumors. Gamit ang tibuok transcriptome (18,270 genes), unom ka ICR genes (IFNG, STAT1, IRF1, CCL5, GZMA, ug CXCL10) ang lakip sa top ten genes nga positibo nga nalangkit sa TCR immune SEQ clonality (Figure 2d). Ang ImmunoSEQ TCR clonality mas kusog nga nakig-uban sa kadaghanan sa mga ICR gene kaysa sa mga correlations nga naobserbahan gamit ang tumor-responsive CD8+ markers (Figure 2f ug 2g). Sa konklusyon, ang pagtuki sa ibabaw nagsugyot nga ang ICR signature nakakuha sa presensya sa tumor-enriched, clonally amplified T cells ug mahimong makapasabut sa prognostic implikasyon niini.
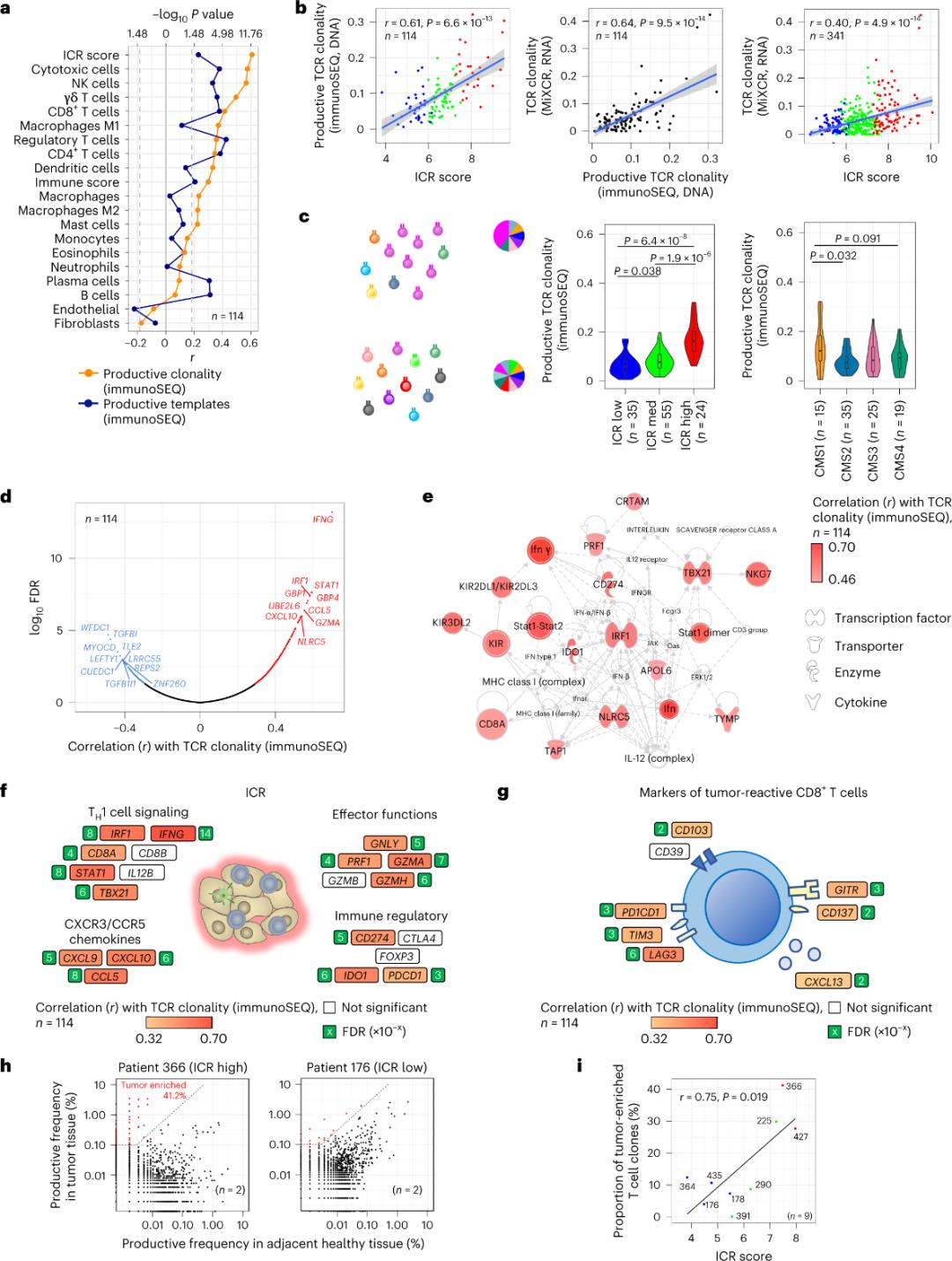
Hulagway 2. Mga sukdanan sa TCR ug korelasyon sa mga gene nga may kalabotan sa resistensya, mga immune ug molekular nga subtype.
Komposisyon sa microbiome sa himsog ug kanser sa colon nga mga tisyu
Ang mga tigdukiduki nagpahigayon og 16S rRNA sequencing gamit ang DNA nga gikuha gikan sa gipares nga tumor ug himsog nga tisyu sa colon gikan sa 246 ka mga pasyente (Figure 3a). Alang sa validation, ang mga tigdukiduki dugang nga nag-analisar sa 16S rRNA gene sequencing data gikan sa dugang nga 42 ka mga sample sa tumor nga walay gipares nga normal nga DNA nga magamit alang sa pag-analisar. Una, gitandi sa mga tigdukiduki ang relatibong kadagaya sa flora tali sa gipares nga mga tumor ug himsog nga tisyu sa colon. Ang Clostridium perfringens miusbaw pag-ayo sa mga tumor kon itandi sa himsog nga mga sample (Figure 3a-3d). Walay dakong kalainan sa alpha diversity (diversity ug kadagaya sa mga espisye sa usa ka sample) tali sa tumor ug himsog nga mga sample, ug usa ka gamay nga pagkunhod sa microbial diversity ang naobserbahan sa mga tumor nga taas og ICR kon itandi sa mga tumor nga ubos og ICR.
Aron mahibal-an ang mga klinikal nga may kalabutan nga asosasyon tali sa mga profile sa mikrobyo ug mga klinikal nga resulta, ang mga tigdukiduki nagtumong sa paggamit sa 16S rRNA gene sequencing data aron mailhan ang mga bahin sa microbiome nga nagtagna sa survival. Sa AC-ICAM246, ang mga tigdukiduki nagpadagan og OS Cox regression model nga mipili og 41 ka mga bahin nga adunay dili-zero nga mga coefficients (nga nalangkit sa differential mortality risk), nga gitawag og MBR classifiers (Figure 3f).
Niining training cohort (ICAM246), ang ubos nga MBR score (MBR<0, ubos nga MBR) nalambigit sa mas ubos nga risgo sa kamatayon (85%). Gikumpirma sa mga tigdukiduki ang asosasyon tali sa ubos nga MBR (risgo) ug dugay nga OS sa duha ka independente nga gi-validate nga cohort (ICAM42 ug TCGA-COAD). (Figure 3) Ang pagtuon nagpakita og kusog nga korelasyon tali sa endogastric cocci ug MBR scores, nga parehas sa tumor ug himsog nga tisyu sa colon.
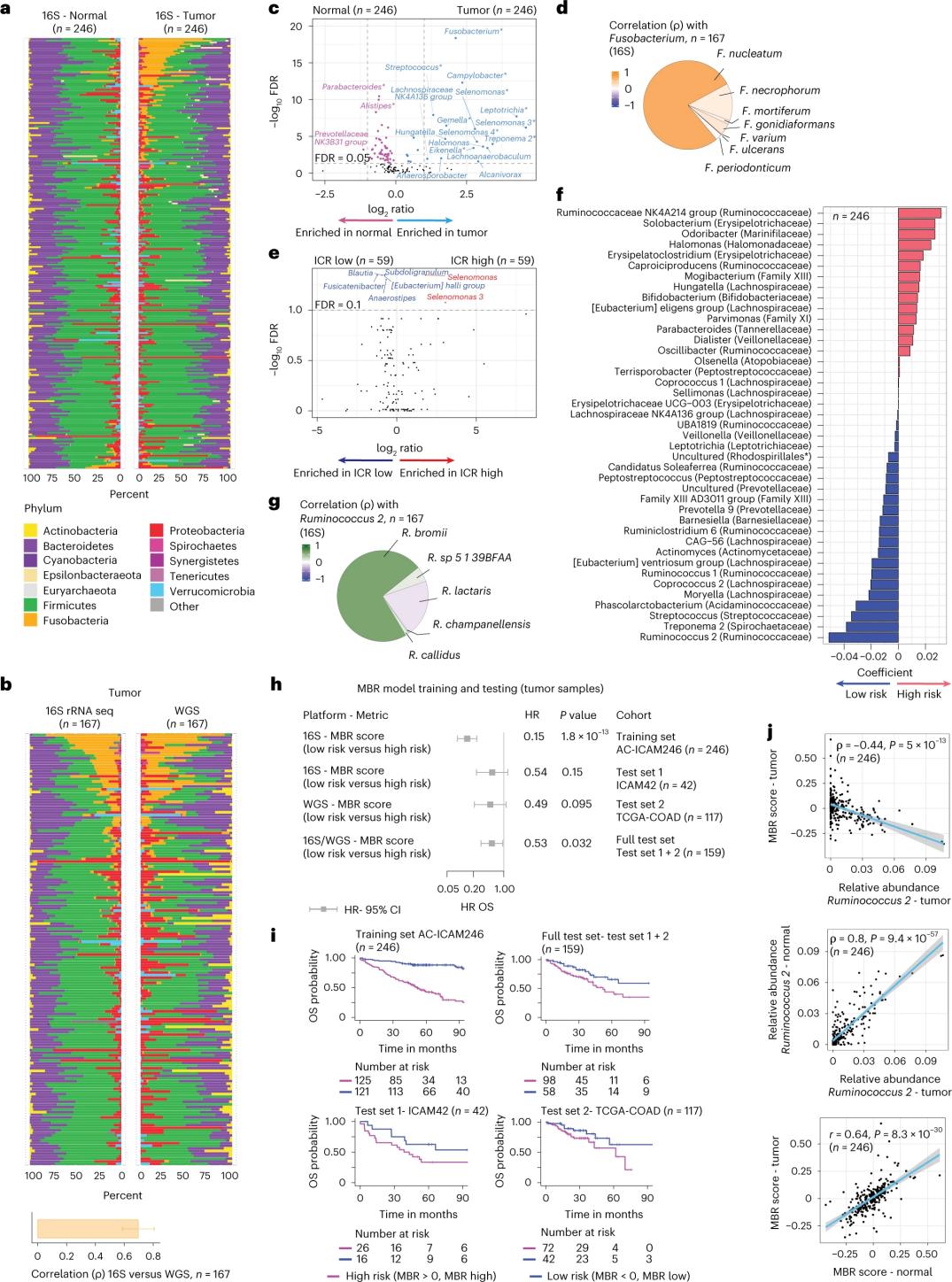
Hulagway 3. Microbiome sa tumor ug himsog nga mga tisyu ug ang relasyon sa ICR ug pagkabuhi sa pasyente.
Konklusyon
Ang pamaagi sa multi-omics nga gigamit niini nga pagtuon nagtugot sa hingpit nga pag-ila ug pag-analisar sa molecular signature sa immune response sa colorectal cancer ug nagpadayag sa interaksyon tali sa microbiome ug sa immune system. Ang lawom nga TCR sequencing sa tumor ug himsog nga mga tisyu nagpadayag nga ang prognostic effect sa ICR mahimong tungod sa abilidad niini sa pagkuha sa tumor-enriched ug posible nga tumor antigen-specific T cell clones.
Pinaagi sa pag-analisar sa komposisyon sa tumor microbiome gamit ang 16S rRNA gene sequencing sa mga sample sa AC-ICAM, ang team nakaila sa usa ka microbiome signature (MBR risk score) nga adunay kusog nga prognostic value. Bisan tuod kini nga signature gikuha gikan sa mga sample sa tumor, adunay kusog nga correlation tali sa himsog nga colorectum ug tumor MBR risk score, nga nagsugyot nga kini nga signature mahimong makakuha sa komposisyon sa gut microbiome sa mga pasyente. Pinaagi sa paghiusa sa ICR ug MBR scores, posible nga mailhan ug mapamatud-an ang usa ka multi-omic student biomarker nga nagtagna sa survival rate sa mga pasyente nga adunay colon cancer. Ang multi-omic dataset sa pagtuon naghatag og kapanguhaan aron mas masabtan ang colon cancer biology ug makatabang sa pagdiskobre sa personalized nga mga pamaagi sa therapeutic.
Oras sa pag-post: Hunyo-15-2023
 中文网站
中文网站